
-

生物通官微
陪你抓住生命科技
跳动的脉搏
MicroMap:人类微生物组代谢网络可视化资源的构建与应用
《npj Biofilms and Microbiomes》:MicroMap: a network visualisation resource for human microbiome metabolism
【字体: 大 中 小 】 时间:2025年11月29日 来源:npj Biofilms and Microbiomes 9.2
编辑推荐:
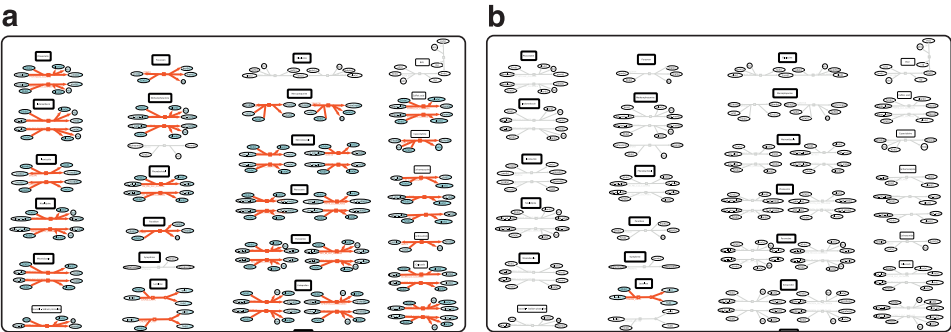
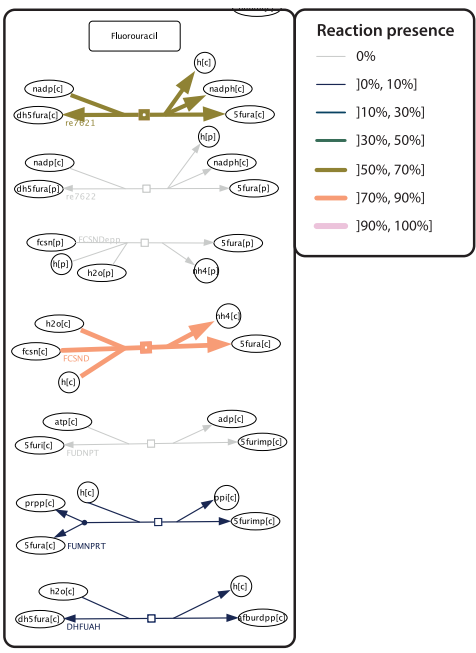
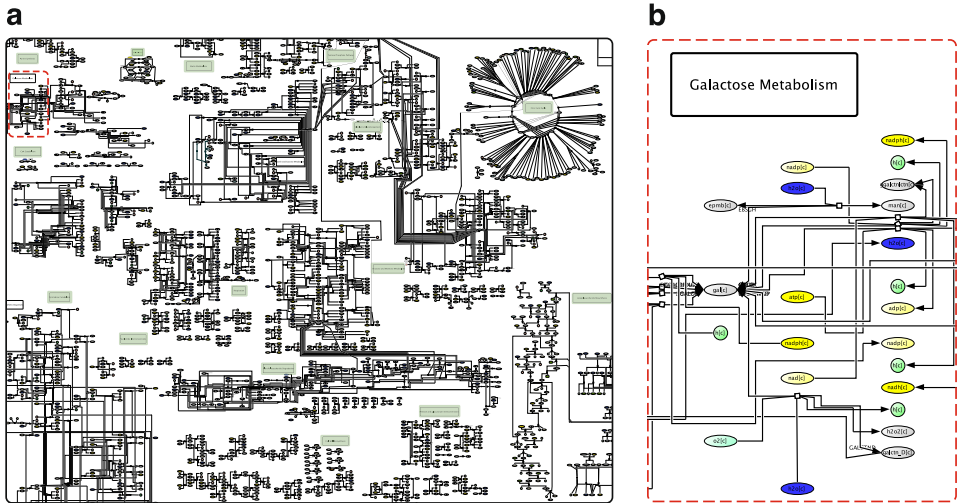
本刊推荐:为填补大规模微生物组代谢网络可视化空白,研究团队开发了MicroMap――首个手工绘制的人类微生物组代谢网络图谱。该资源整合AGORA2和APOLLO数据库中257,429个微生物基因组尺度代谢模型(GEM),涵盖5,064个独特反应和3,499个代谢物(含98种药物代谢)。通过约束性重构与分析(COBRA)框架,支持代谢通量可视化、菌群代谢能力比较及动态动画展示,为营养-宿主-微生物组-疾病轴研究提供机制性假说生成平台。
 生物通微信公众号
生物通微信公众号